Denkt man an die DNA, erscheinen vor dem geistigen Auge direkt zwei Stränge, welche in sich zusammen verwoben, eine helikale Struktur bilden. Sie taucht immer wieder in den Nachrichten, Filmen oder in Werbungen auf, bei welchen versucht wird, molekularbiologische Sachverhalte simpel darzustellen. Dass wir diese Struktur heutzutage für eine Selbstverständlichkeit halten, beruht jedoch auf Jahre langer und komplexer Forschung, die nur mit Hilfe vieler Arbeitsgruppen zu bewältigen war. Warum ist diese Struktur so bedeutsam? Man sollte nicht außer Acht lassen, dass es sich hier um unser aller Erbgut handelt, dem Material, welches unseren gesamten und individuellen Bauplan enthält. Außerdem lassen sich durch die Struktur Rückschlüsse auf die Funktion ziehen. – Betrachten wir als Metapher zum Beispiel unsere Hände: Die Tatsache, dass wir mit unseren Händen Dinge auf eine bestimmte Art und Weise greifen und halten können, ist nur durch die Struktur der Hände möglich, also durch ihren Aufbau mit Handfläche, Fingern, Gelenken, Knorpeln etc. Man muss also in die Tiefe der Struktur gehen, um zu verstehen, warum Hände so funktionieren, wie sie es tun. – Und so hilft uns die Struktur der DNA bei der Beantwortung von fundamentalen Fragen des Lebens wie „Was sind Gene?“, „Wie sind sie in der DNA gespeichert?“ und „Wie kann sich die DNA vermehren?“.
Vor der Veröffentlichung der DNA-Struktur wusste man bereits durch die Arbeiten von Albrecht Kössel und Emil Fischer, dass sich die DNA aus den Basen Adenin (A), Guanin (G), Cytosin (C) und Thymin (T) sowie einem Kohlenhydrat und der Phosphorsäure zusammensetzt. Deren Strukturen hatte man zum Großteil einzeln bereits gelöst. Phoebus Levene war es schließlich, der den letzten Bestandteil, den Zucker, als Desoxyribose erkannte. Nur wenige Jahre später konnte Oswald T. Avery nachweisen, dass es sich bei diesem Molekül um den Träger der Erbinformation handelt, und Erwin Chargaff erkannte den außergewöhnlichen Zusammenhang, dass die Basen Adenin und Thymin sowie Guanin und Cytosin in der DNA unterschiedlichster Organismen immer in denselben Verhältnissen vorkommen.
Diese Entdeckungen waren der Startschuss, dass viele Arbeitsgruppen auf der ganzen Welt begannen, an der Strukturaufklärung der DNA zu forschen. Doch wie läuft eine solche Strukturaufklärung von einzelnen für das menschliche Auge nicht sichtbaren Molekülen ab? Die weit verbreitetste Methode zu der Zeit war die Kristallstrukturanalyse (X-ray crystallography). Wie der Name bereits vermuten lässt, wird hierfür das Molekül, dessen Struktur man entschlüsseln möchte, in kristalliner Form benötigt. Als Kristall bezeichnet man einen Feststoff, dessen Bestandteile (Atome, Ione oder Moleküle) regelmäßig in einem Gitter vorliegen. Um in Wasser isolierte DNA in einen Kristall zu zwängen, muss man lediglich das Wasser unter langsamen und kontrollierten Bedingungen evaporieren, also verdunsten, lassen. Ähnlich, jedoch schneller, wird es bei der Gewinnung von Salz-Kristallen aus Meerwasser gemacht. Der gewonnene Kristall mit DNA wird im Anschluss Röntgenstrahlen ausgesetzt. Diese Strahlen gelangen durch den Kristall und werden auf einer Projektionsfläche (Röntgenfilm) aufgefangen. Treffen die Strahlen in dem Kristall jedoch auf Elektronen, werden diese abgeleitet. Eine solche Ableitung von Strahlung an einem Hindernis wird auch Beugung oder Diffraktion genannt. So entsteht auf den Röntgenfilmen für jeden Molekül-Kristall ein spezifisches Muster. Dieses Muster wird auch Beugungsmuster (engl.: „Diffractionpattern“) genannt. Aus diesem Substanz-spezifischen Beugungsmuster kann nun mit Hilfe komplexer mathematischer Berechnungen eine Karte der Elektronendichte berechnet werden. In dieser können im Anschluss die einzelnen Atome passend eingefügt werden und man erhält die Struktur des gewünschten Moleküls.
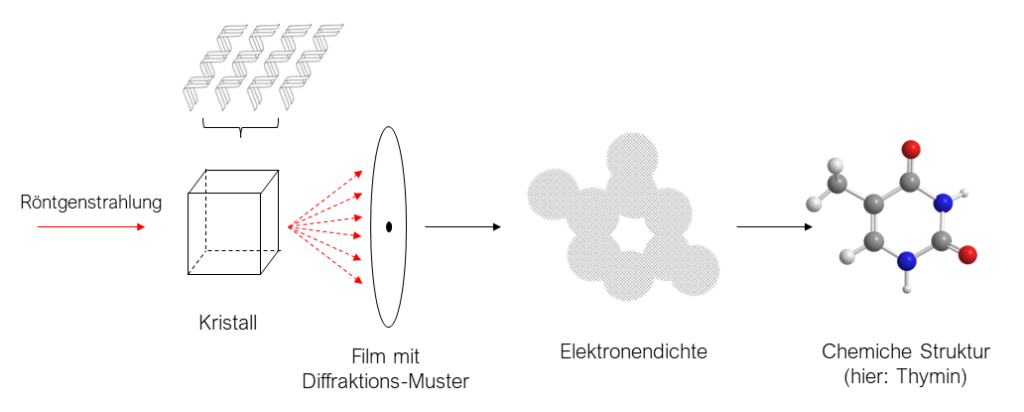
Die ersten Röntgenbeugungsmuster der DNA wurden von William Astbury erstellt, dessen Arbeiten von Rosalind Franklin und Maurice Wilkins weitergeführt wurden. Im Jahre 1951 zeigte Wilkins seine Röntgenstrukturaufnahmen auf einer Tagung in Neapel und vermutete aus diesen einen schraubenartigen Aufbau ableiten zu können. Zur gleichen Zeit gelang es Rosalind Franklin, weitere und präzisere Röntgenstrukturaufnahmen der DNA zu generieren. Ebenso erschien eine Publikation von Linus Pauling, in welcher er als erster zeigen konnte, dass Proteine eine helikale Struktur annehmen können, dass sie also wie eine Strickleiter um sich selbst gewoben sein können. Es waren schließlich James Watson und Francis Crick, welche 1953 die bekannten Informationen zusammentrugen und ein auf diese Informationen basierendes Modell der DNA erstellten. Dieses Modell zeigte die DNA als eine Doppel-Helix, welche aus zwei anti-parallelen Strängen besteht. Die sich wiederholende Verbindung aus Phosphorsäure und Desoxyribose bildet dabei das Rückgrat. An jeder Desoxyribose ist zudem eine der vier Basen (A, T, C & G) gebunden. Sie bilden das Innere der Doppel-Helix und halten die beiden Stränge über Wasserstoff-Brücken-Bindungen zusammen (gestrichelte Linien in der Abbildung). So bilden die Basen Adenin und Thymin untereinander Wasserstoff-Brückenbindungen aus, sowie die Basen Guanin und Cytosin. Diese strukturbildende chemische Grundlage begründet nebenbei die zuvor erwähnten Entdeckungen Erwin Chargaffs über das Verhältnis der einzelnen Basen zueinander. Führende Wissenschaftler, die sich mit der Struktur der DNA beschäftigten, vermuteten lange, dass es sich bei der DNA eher um einen einfachen Strang oder um einen Komplex aus drei Strängen handelt, bei welchem das Zucker-Phosphat Rückgrat ins Innere zeigte. Die Röntgenstrukturaufnahmen der Wissenschaftlerin Rosalind Franklind waren es jedoch, welche eine Doppel-Helix als Struktur annehmen ließen. Diese Aufnahmen, welche ohne das Einverständnis von R. Franklind durch M. Wilkins an J. Watson und F. Crick gelangten, bildeten eine fundamentale Grundlage in dem theoretischen DNA-Modell von Watson und Crick. Noch im selben Jahr publizierte Rosalind Franklind ihre Ergebnisse der Kristallstrukturanalyse und lieferte den experimentellen Nachweis zu den Annahmen der DNA-Struktur von J. Watson und F. Crick.

Im Jahre 1962 erhielten J. Watson, F. Crick und M. Wilkins den Nobelpreis für Medizin für ihre bahnbrechende Entdeckung, welche von vielen als Start der Molekular-Biologie betrachtet wird. Rosalind Franklin, welche mit ihren Röntgenstrukturaufnahmen den wesentlichen Beitrag für diese Entdeckung leistete, verstarb 1958 und wurde deswegen, nach den Regeln des Nobelkomitees, nicht mit dem Nobelpreis ausgezeichnet.
Autor: SV Literatur Pauling L & Robert CB (1950) Two hydrogen-bonded spiral configurations of the polypeptide chain. J. Am. Chem. Soc., vol. 72, pp. 5349. Watson JD & Crick FHC (1953) Molecular Structure of Nucleic Acids. A structure for deoxyribose nucleic acid. Nature, vol. 171, pp. 737-738. Wilkins MHF, Stokes AR, Wilson HR (1953) Molecular structure of deoxypentose nucleic acids. Nature, vol. 171, pp. 738-740. Franklin RE & Raymond GG (1953) Molecular configuration in sodium thymonucleate. Nature, vol. 171, pp. 740-741. Watson JD & Crick FHC (1953) Genetical implications of the structure of desoxyribonucleic acid. Nature, vol. 171, pp. 964-967. Franklin RE, Gosling RG (1953) Evidence for 2-chain helix in crystalline structure of sodium deoxyribonucleate. Nature, vol. 172, pp. 156-157. Harding S (2019) H-bonds and DNA. Biochem, vol. 41, pp. 38-41. [/et_pb_text][/et_pb_column][/et_pb_row][/et_pb_section]
Hi there to every body, it’s my first visit of this web site;
this weblog includes amazing and genuinely excellent
data for readers.